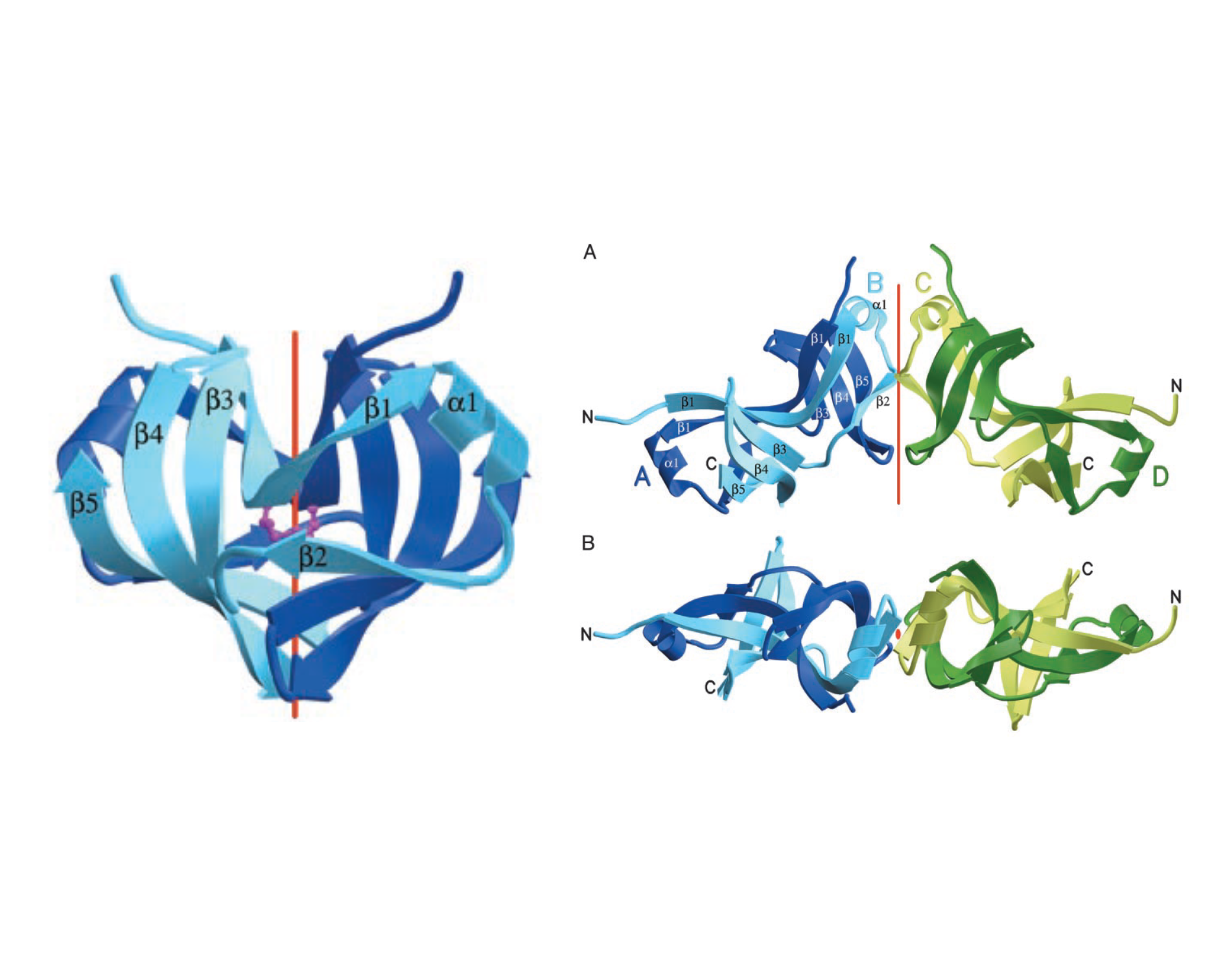
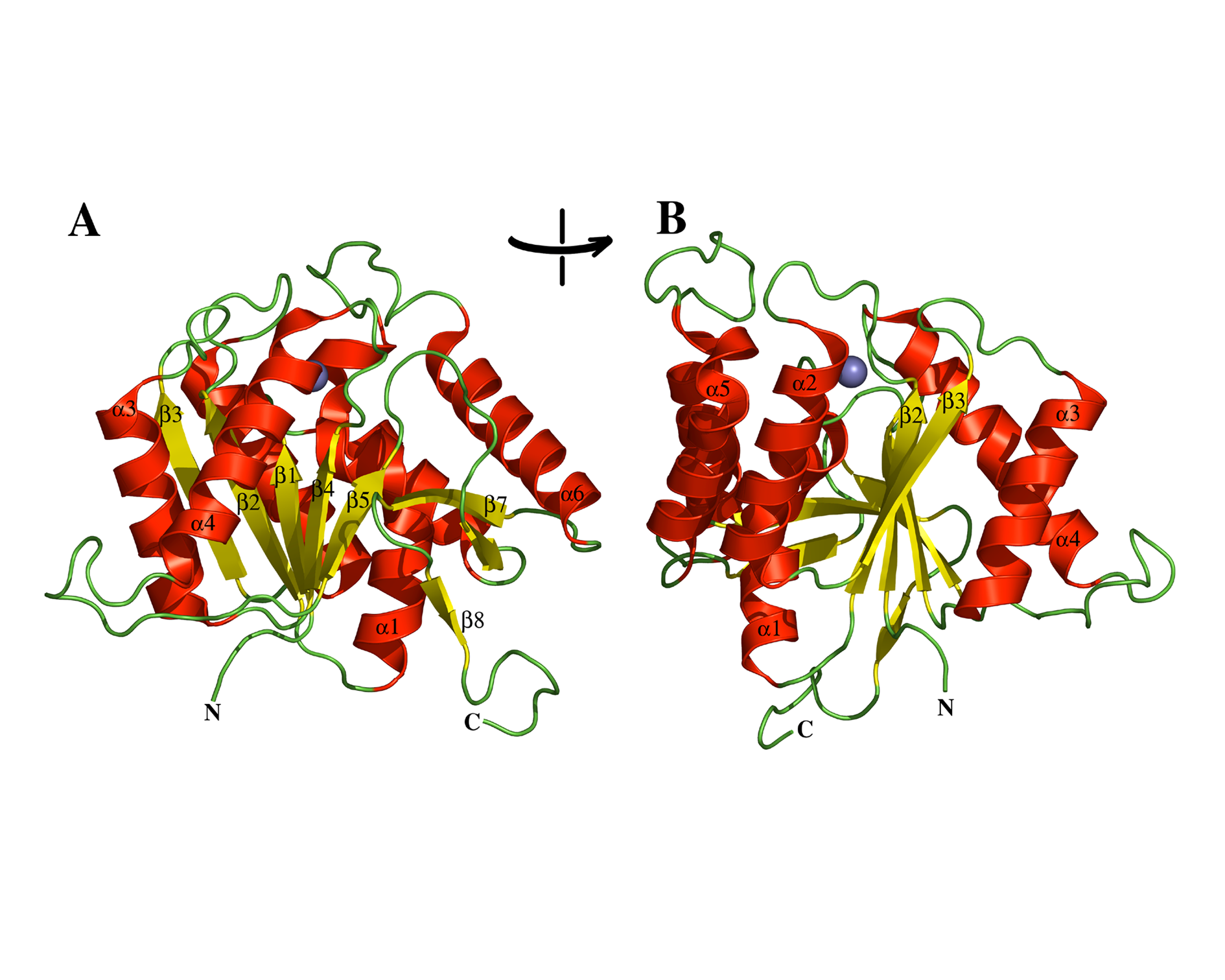
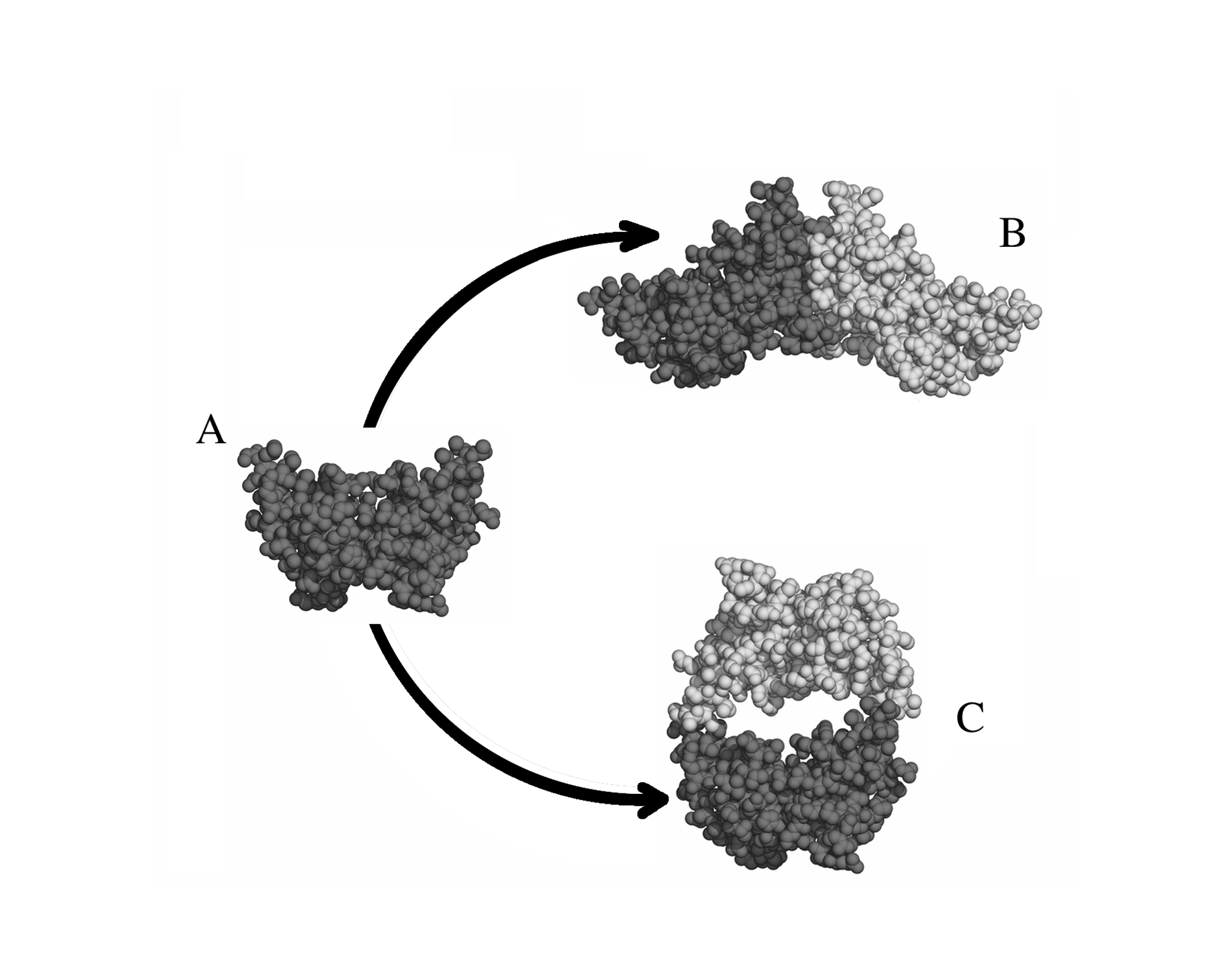
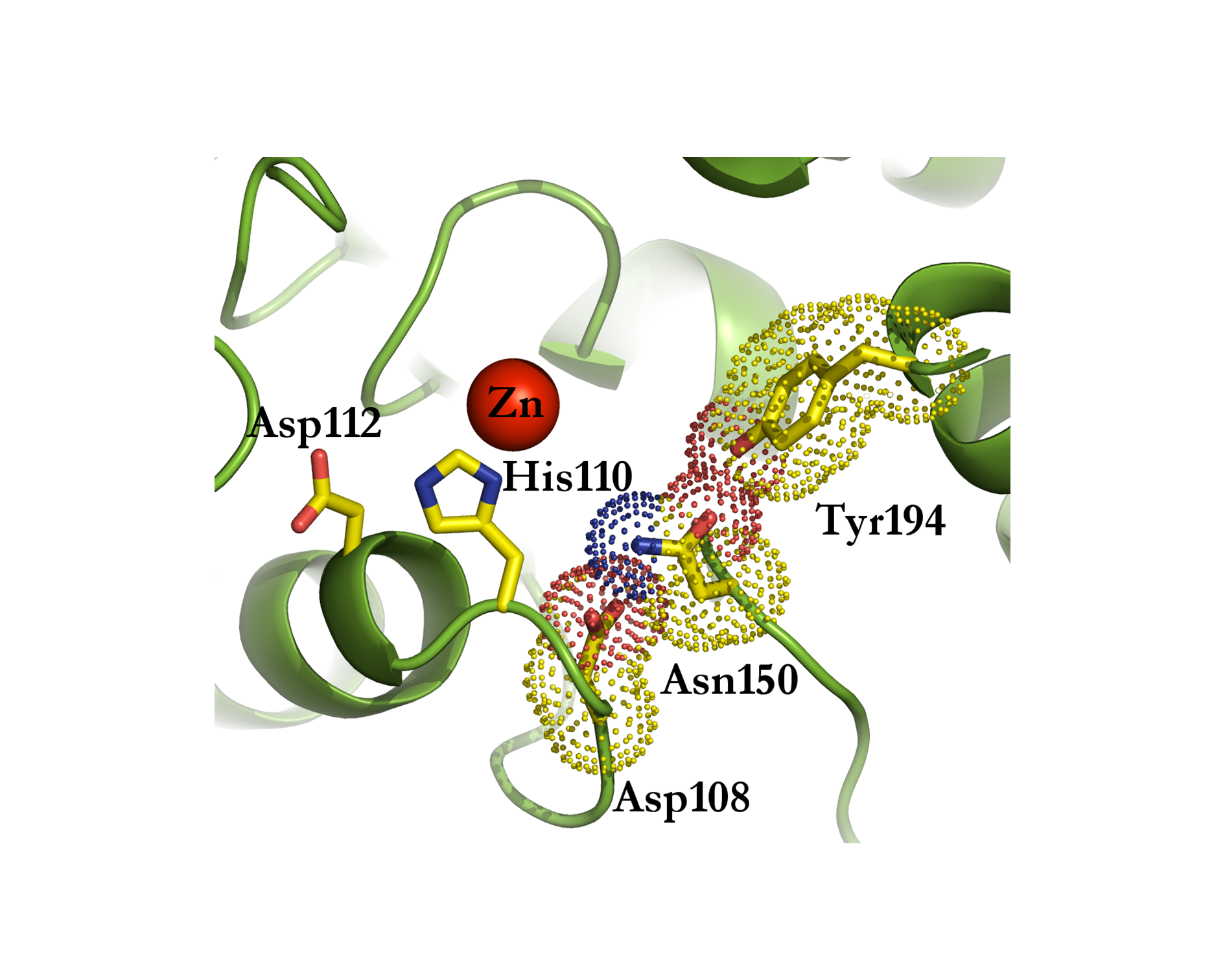
Σύντομη περιγραφή
Το Εργαστήριο Βιομοριακής Δομής και Βιοφυσικής Ανάλυσης ιδρύθηκε με το ΦΕΚ 1575/27-07-2015 τ.Β και θεραπεύει το εκπαιδευτικό, εργαστηριακό και ερευνητικό έργο του Τμήματος Μοριακής Βιολογίας και Γενετικής στα γνωστικά αντικείμενα της Δομικής Βιολογίας (προσδιορισμός 3D δομής πρωτεϊνών και νουκλεοπρωτεϊνικών συμπλόκων με κρυσταλλογραφία ακτίνων Χ), Πρωτεϊνικής Βιοχημείας (υπερέκφραση και απομόνωση με χρωματογραφικές μεθόδους βιομορίων), Μελέτης και χαρακτηρισμού της δομής-λειτουργίας Ενζύμων, Δομικής Βιοπληροφορικής (μελέτη δομής-λειτουργίας με υπολογιστικές μεθόδους) και Βιοφυσικής. Το ερευνητικό έργο εκπονείται στις εγκαταστάσεις που βρίσκονται στο 2ο όροφο του κτηρίου του Τμήματος Μοριακής Βιολογίας και Γενετικής και αποτελούνται από ένα εργαστήριο εξοπλισμένο κατάλληλα για πραγματοποίηση υπερέκφρασης πρωτεϊνών σε βακτηριακούς φορείς, χρωματογραφικής απομόνωσης και κρυστάλλωσης βιομορίων.
Η ερευνητική δραστηριότητα του εργαστηρίου εστιάζει στη μελέτη της σχέσης δομής-λειτουργίας των πρωτεϊνών μέσω του προσδιορισμού της τρισδιάστατης δομής σε ατομική διακριτικότητα. Ιδιαίτερο ενδιαφέρον έχει για εμάς η διερεύνηση των μηχανισμών μέσω των οποίων μικρές αλλαγές—όπως μια σημειακή μετάλλαξη ή μια μικρή μετατόπιση κάποιου δομικού στοιχείου—μπορούν να αλλάξουν δραματικά τη λειτουργία των πρωτεϊνών και να συνεισφέρουν στην υγεία και την ασθένεια. Συγκεκριμένα ερωτήματα που διερευνούμε στο εργαστήριο ειναι:
- Πώς οι μεταλλάξεις ή οι χημικές τροποποιήσεις (π.χ. μετα-μεταφραστικές) επηρεάζουν τη λειτουργία/δραστικότητα των πρωτεϊνών/ενζύμων;
- Ποιοί είναι οι μοριακοί μηχανισμοί που καθορίζουν τις μακρομοριακές αλληλεπιδράσεις;
- Ποια είναι η ατομική βάση της μοριακής αναγνώρισης;
- Ποια είναι η σημασία της δομικής ευελιξίας των πρωτεϊνών στη λειτουργία τους;
- Πώς συνδέονται οι δομικές πρωτεϊνικές αλλαγές με βιοχημικούς μηχανισμούς;
- Ποιο είναι το βιολογικό νόημα των ψευδοενζύμων, των πρωτεϊνών με δευτερεύουσες λειτουργίες (moonlighting) και των μεταμορφικών πρωτεϊνών;
Η προσέγγισή μας συνδυάζει ένα ευρύ φάσμα πειραματικών και υπολογιστικών μεθόδων όπως: Βιοχημεία πρωτεϊνών και υγρή χρωματογραφία, Μοριακή βιολογία και ενζυμολογία, Κρυσταλλογραφία ακτίνων-Χ (X-raycrystallography) και άλλες βιοφυσικές μέθοδους, Δομική βιοπληροφορική και μοριακή αγκυροβόληση (moleculardocking) κ.α.
- Υπερέκφραση και απομόνωση πρωτεϊνών,
- βιοφυσικός χαρακτηρισμός πρωτεϊνών και συμπλόκων τους,
- Προσδιορισμός πρωτεϊνικών δομών και συμπλόκων τους με κρυσταλλογραφία ακτίνων Χ.
- InTechThrace: Integrated Technologies in biomedical research: multilevel biomarker analysis in Thrace. Operational Program “Competitiveness, Entrepreneurship & Innovation, 2014-2020 (EPAnEK)”. (member, 2022-2023).
- POLYPEPPHARM: Improved generic polypeptide drugs with innovative pharmaceutical forms. Operational Programme “Competitiveness, Entrepreneurship and Innovation,2014-2020 (EPAnEK)”. (member, 2021-2023).
- Molfetas AS, Boutris N, Tomatsidou A, Kokkinidis M, Fadouloglou VE. Variations of the NodB Architecture Are Attuned to Functional Specificities into and beyond the Carbohydrate Esterase Family 4. Biomolecules. 2024 Mar 8;14(3):325. doi: 10.3390/biom14030325. PMID: 38540745; PMCID: PMC10967932.
- Litso I, Plaitakis A, Fadouloglou VE, Providaki M, Kokkinidis M, Zaganas I. Structural Evolution of Primate Glutamate Dehydrogenase 2 as Revealed by In Silico Predictions and Experimentally Determined Structures. Biomolecules. 2023 Dec 23;14(1):22. doi: 10.3390/biom14010022. PMID: 38254622; PMCID: PMC10812971.
- Xanthis V, Mantso T, Dimtsi A, Pappa A, Fadouloglou VE. Human Aldehyde Dehydrogenases: A Superfamily of Similar Yet Different Proteins Highly Related to Cancer. Cancers (Basel). 2023 Sep 4;15(17):4419. doi: 10.3390/cancers15174419. PMID: 37686694; PMCID: PMC10650815.
- Makraki E, Miliara S, Pagkalos M, Kokkinidis M, Mylonas E, Fadouloglou VE. Probing the conformational changes of in vivo overexpressed cell cycle regulator 6S ncRNA. Front Mol Biosci. 2023 Jul 17;10:1219668. doi: 10.3389/fmolb.2023.1219668. PMID: 37555016; PMCID: PMC10406553.
- Voulgaridou GP, Theologidis V, Xanthis V, Papagiannaki E, Tsochantaridis I, Fadouloglou VE, Pappa A. Identification of a peptide ligand for human ALDH3A1 through peptide phage display: Prediction and characterization of protein interaction sites and inhibition of ALDH3A1 enzymatic activity. Front Mol Biosci. 2023 Mar 20;10:1161111. doi: 10.3389/fmolb.2023.1161111. PMID: 37021113; PMCID: PMC10067601.
- Gazi AD, Kokkinidis M, Fadouloglou VE. α-Helices in the Type III Secretion Effectors: A Prevalent Feature with Versatile Roles. Int J Mol Sci. 2021 May 21;22(11):5412. doi: 10.3390/ijms22115412. PMID: 34063760; PMCID: PMC8196651.
- Amprazi M, Tomatsidou A, Paliogianni D and Fadouloglou VE. Post-Translational Modifications: Host Defence Mechanism, Pathogenic Weapon, and Emerged Target of Anti-Infective Drugs, in book: Frontiers in Anti-Infective Drug Discovery, Volume 9, pp: 25-122 (98), doi: 10.2174/9781681088297121090004.
- Dimovasili C, Fadouloglou VE, Kefala A, Providaki M, Kotsifaki D, Kanavouras K, Sarrou I, Plaitakis A, Zaganas I, Kokkinidis M. Crystal structure of glutamate dehydrogenase 2, a positively selected novel human enzyme involved in brain biology and cancer pathophysiology. J Neurochem. 2021 May;157(3):802-815. doi: 10.1111/jnc.15296. Epub 2021 Jan 23. PMID: 33421122.
- Kokkinidis M, Glykos NM, Fadouloglou VE. Catalytic activity regulation through post-translational modification: the expanding universe of protein diversity. Adv Protein Chem Struct Biol. 2020;122:97-125. doi: 10.1016/bs.apcsb.2020.05.001. Epub 2020 Jun 27. PMID: 32951817; PMCID: PMC7320668.
- Khalid RR, Maryam A, Fadouloglou VE, Siddiqi AR, Zhang Y. Cryo-EM density map fitting driven in-silico structure of human soluble guanylate cyclase (hsGC) reveals functional aspects of inter-domain cross talk upon NO binding. J Mol Graph Model. 2019 Jul;90:109-119. doi: 10.1016/j.jmgm.2019.04.009. Epub 2019 Apr 24. PMID: 31055154; PMCID: PMC7956049.
- Fadouloglou VE, Balomenou S, Aivaliotis M, Kotsifaki D, Arnaouteli S, Tomatsidou A, Efstathiou G, Kountourakis N, Miliara S, Griniezaki M, Tsalafouta A, Pergantis SA, Boneca IG, Glykos NM, Bouriotis V, Kokkinidis M. Unusual α-Carbon Hydroxylation of Proline Promotes Active-Site Maturation. J Am Chem Soc. 2017 Apr 19;139(15):5330-5337. doi: 10.1021/jacs.6b12209. Epub 2017 Apr 5. PMID: 28333455.
- Fadouloglou VE, Lin HT, Tria G, Hernández H, Robinson CV, Svergun DI, Luisi BF. Maturation of 6S regulatory RNA to a highly elongated structure. FEBS J. 2015 Dec;282(23):4548-64. doi: 10.1111/febs.13516. Epub 2015 Oct 13. PMID: 26367381; PMCID: PMC7610929.
- Balomenou S, Arnaouteli S, Koutsioulis D, Fadouloglou VE and Bouriotis V. Deacetylases: New Antibacterial Drug Targets. in book: Frontiers in Anti-Infective Drug Discovery , pp: 68-130 (63), doi: 10.2174/9781681080826115040005.
- Fadouloglou VE. Electroelution of nucleic acids from polyacrylamide gels: a custom-made, agarose-based electroeluter. Anal Biochem. 2013 Jun 1;437(1):49-51. doi: 10.1016/j.ab.2013.02.021. Epub 2013 Mar 7. PMID: 23499972.
- Fadouloglou VE, Kapanidou M, Agiomirgianaki A, Arnaouteli S, Bouriotis V, Glykos NM, Kokkinidis M. Structure determination through homology modelling and torsion-angle simulated annealing: application to a polysaccharide deacetylase from Bacillus cereus. Acta Crystallogr D Biol Crystallogr. 2013 Feb;69(Pt 2):276-83. doi: 10.1107/S0907444912045829. Epub 2013 Jan 19. PMID: 23385463.
- Charova SN, Gazi AD, Kotzabasaki M, Sarris PF, Fadouloglou VE, Panopoulos NJ and Kokkinidis M. Protein Flexibility and Coiled-Coil Propensity: New Insights Into Type III and Other Bacterial Secretion Systems. In book: Biochemistry, Edited by Deniz Ekinci, 2012 March. doi: 10.5772/32582.
- Gazi AD, Sarris PF, Fadouloglou VE, Charova SN, Mathioudakis N, Panopoulos NJ, Kokkinidis M. Phylogenetic analysis of a gene cluster encoding an additional, rhizobial-like type III secretion system that is narrowly distributed among Pseudomonas syringae strains. BMC Microbiol. 2012 Sep 2;12:188. doi: 10.1186/1471-2180-12-188. PMID: 22937899; PMCID: PMC3574062.
- Kokkinidis M, Glykos NM, Fadouloglou VE. Protein flexibility and enzymatic catalysis. Adv Protein Chem Struct Biol. 2012;87:181-218. doi: 10.1016/B978-0-12-398312-1.00007-X. PMID: 22607756.
- Deli A, Koutsioulis D, Fadouloglou VE, Spiliotopoulou P, Balomenou S, Arnaouteli S, Tzanodaskalaki M, Mavromatis K, Kokkinidis M and Bouriotis V (2010) LmbE proteins from Bacillus cereus are de-N-acetylases with broad substrate specificity and are highly similar to proteins in Bacillus anthracis, FEBS J. 277, 2740-2753.
- Fadouloglou VE, Stavrakoudis A, Bouriotis V, Kokkinidis M and Glykos NM (2009) Molecular dynamics simulations of BcZBP, a deacetylase from Bacillus cereus. Active site loops determine substrate accessibility and specificity J. Chem. Theory Comput. 5, 3299-3311.
- Fadouloglou VE, Bastaki MN, Ashcroft AE, Phillips SEV, Panopoulos NJ, Glykos NM and Kokkinidis M (2009) On the quaternary association of the type III secretion system HrcQB-C protein: Experimental evidence differentiates among the various oligomerization models J. Struct. Biol. 166, 214-25.
- Fadouloglou VE, Kokkinidis M & Glykos NM (2008) Determination of protein oligomerization state: Two approaches based on glutaraldehyde crosslinking Anal. Biochem 373, 404-406.
- Fadouloglou VE, Deli A, Glykos NM, Psylinakis E, Bouriotis V & Kokkinidis M (2007) Crystal structure of the BcZBP, a zinc-binding protein from Bacillus cereus: functional insights from structural data, FEBS J. 274, 3044-3054.
- Fadouloglou VE, Kotsifaki D, Gazi AD, Fellas G, Meramveliotaki C, Deli A, Psylinakis E, Bouriotis V & Kokkinidis M (2006) Purification, crystallization and preliminary characterization of a putative LmbE-like deacetylase from Bacillus cereus, Acta Cryst. F62, 261-264.
- Tampakaki AP, Fadouloglou VE, Gazi A.D., Panopoulos N.J. & Kokkinidis M. (2004) Conserved features of type III secretion, Cell. Microbiol., 6, 805-816.
- Papanikolaou Y, Kotsifaki D, Gazi AD, Fadouloglou VE, Glykos NM, Cesareni G & Kokkinidis M (2004) Ionic strength reducers: an efficient approach to protein purification and crystallization. Application to two Rop variants, Acta Cryst. D60, 1334-1337.
- Fadouloglou VE, Tampakaki A, Glykos NM, Bastaki MN, Hadden J, Phillips SEV, Panopoulos N & Kokkinidis M (2004) Structure of HrcQB-C, a conserved component of the bacterial type III secretion systems, Proc. Natl. Acad. Sci. USA 101, 70-75.
- Fadouloglou VE, Tampakaki A, Panopoulos N & Kokkinidis M (2001) Structural studies of the Hrp secretion system: expression, purification, crystallization and preliminary X-ray analysis of the C-terminal domain of the HrcQBprotein from Pseudomonas syringae pv. phaseolicola, Acta Cryst., D57, 1689-1691.
- Fadouloglou VE, Glykos NM & Kokkinidis M (2001) Side-chain conformations in 4-a-helical bundles, Protein Eng., 14 (5), 321-328.
- Fadouloglou VE, Glykos NM & Kokkinidis M (2000) A fast and inexpensive procedure for drying polyacrylamide gels, Anαl. Biochem., 287, 185-186.
- Spyridaki A, Glykos NM, Kotsifaki D, Fadouloglou VE & Kokkinidis M (2000) Crystallization and diffraction to ultrahigh resolution (0.8Å) of a designed variant of the Rop protein, Acta Cryst., D56, 1015-1016.
No data found.
| Ονοματεπώνυμο | Ιδιότητα |
|---|---|
| Στογιαννούδη Μαρκέλλα | Μεταπτυχιακή Φοιτήτρια |
| Χαϊδά Μάρθα | Μεταπτυχιακή Φοιτήτρια |
| Ποντίκη Δήμητρα | Μεταπτυχιακή Φοιτήτρια |
| Γερασίμου Χρήστος | Μεταπτυχιακός Φοιτητής |
| Τερζενίδης Μιχάλης | Προπτυχιακός Φοιτητής |
| Ασημακοπούλου Γεωργία | Προπτυχιακή Φοιτήτρια |
No data found.
Πληροφορίες
Διευθύντρια
Φαδούλογλου Βασιλική, Αναπληρώτρια Καθηγήτρια
Τμήμα Μοριακής Βιολογίας και Γενετικής, ΔΠΘ, Kτίριο Φώτης Καφάτος, Πανεπιστημιούπολη, περιοχή Δραγάνα, 68100 Αλεξανδρούπολη