Σύντομη περιγραφή
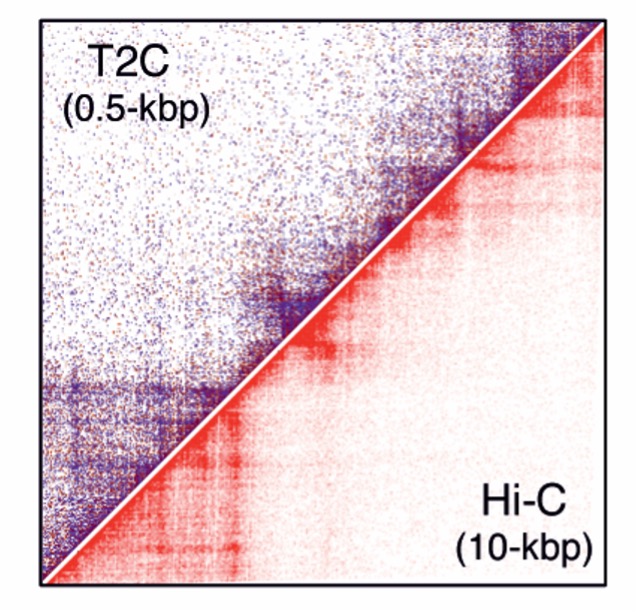
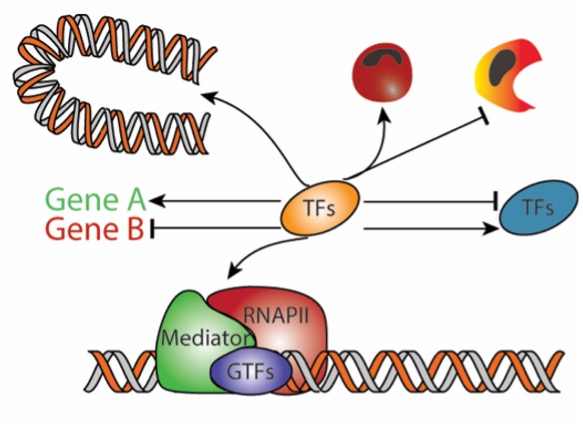
Το ερευνητικό ενδιαφέρον του εργαστηρίου εδράζεται στον κλάδο της Μοριακής Βιολογίας -Βιολογίας Συστημάτων. Συγκεκριμένα, μελετάμε σύνθετες αναπτυξιακές διεργασίες ή/και διεργασίες διαφοροποίησης σε ποικίλα βιολογικά συστήματα. Επίσης μελετάμε τον διττό ρόλο και την δυναμική των σύνθετων δικτύων μεταγραφικών παραγόντων και των επιγενετικών μηχανισμών, σε σχέση με τον (συνδυασμένο) ρόλο τους στην ρύθμιση της γονιδιακής έκφρασης καθώς και στην χωροχρονική οργάνωση της αρχιτεκτονικής της χρωματίνης. Ακόμα μελετούμε το πλούτο και την ποικιλομορφία της μικροβιακής κοινότητας μέσω της μελέτης του μικροβιώματος, με σκοπό την κατανόηση του, την αποκάλυψη των ιδιοτήτων του, καθώς και την ανακάλυψη τυχόν μικροβιακής υπογραφής συγκεκριμένων προϊόντων. Επίσης χρησιμοποιούμε το eDNA για την χωροχρονική ανάλυση της βιοποικιλότητας των θαλάσσιων περιοχών. Επίσης αναλύουμε του γονιδιώματα βακτηρίων, ώστε να μπορούμε να τα ταξινομούμε φυλογενετικά, να τα κατηγοριοποιούμε in silico, καθώς και να προβλέπουμε in silico τις ενδεχόμενες προβιοτικές τους ιδιότητες ή και ιδιότητες σχετικά με την υγεία μας.
Για την επίτευξη όλων των ανωτέρω στόχων, πέρα από το τις πειραματικές διεργασίες, χρησιμοποιούμε γλώσσες προγραμματισμού, την υπολογιστική βιολογία και βιοπληροφορικές προσεγγίσεις για την ανάλυση και επεξεργασία των δεδομένων.
Χρησιμοποιώντας ολιστικές προσεγγίσεις, μπορούμε να επανασχεδιάσουμε τον τρόπο με τον οποίο προσεγγίζουμε τις δυναμικές αλληλεπιδράσεις ανάμεσα στα συστατικά του κυττάρου και μεταξύ του κυττάρου και του περιβάλλοντος του, οδηγώντας στην δημιουργία βιολογικών δικτύων και αποσαφηνίζοντας τις ιδιότητες των βιολογικών συστημάτων.
- Μελέτη της δυναμικής των μεταγραφικών παραγόντων
- Χωροχρονική οργάνωση της αρχιτεκτονικής της χρωματίνης
- Επιγενετική και σχέση της με την ρύθμιση της γονιδιακής έκφρασης
- Μελέτη μικροοργανισμών (ανάλυση/χαρτογράφηση γονιδιώματος κτλ) και ανάλυση μικροβιώματος
- Ανάλυση μικροβιώματος και γονιδιώματος μικροοργανισμών
- Βιοπληροφορική
- eDNA
- 2024-παρόν Εμβληματική δράση για βιώσιμα αγροδιατροφικά συστήματα – Εφαρμοσμένη Έρευνα, ανάπτυξη υποδομών και υπηρεσιών για την βιωσιμότητα του κλάδου (Sus.Agri.Food), ΓΓΕΚ. ΕΥ για το ΔΠΘ: Καθηγητής Ιωάννης Κουρκουτάς, ΠΚ: Μέλος ομάδας έργου
- 2024-παρόν Novel Biotechnological Solutions in Climate Change Mitigation (BIOSHIELD), Erasmus+ ΕΥ για το ΔΠΘ: Καθηγητής Ιωάννης Κουρκουτάς ΠΚ: Μέλος ομάδας έργου
- 2023-2025 Εφαρμογή της τεχνολογίας eDNA για την παρακολούθηση των ιχθυοαποθεμάτων και των γενετικών πόρων του υδάτινου περιβάλλοντος του Θρακικού Πελάγους ως εργαλείο αειφορικής διαχείρισης (ECOeDNA), Πράσινο Ταμείο. ΠΚ: ΕΥ
- 2023-2025 Βελτίωση της κατάστασης διατήρησης του Pinus Heldreichii σε εθνικό επίπεδο μέσω παραδοσιακών (πολλαπλασιασμό) και καινοτόμων μεθόδων (genotyping), Πράσινο Ταμείο. ΕΥ: Καθηγητής Αριστοτέλης Παπαγεωργίου ΠΚ: Μέλος ομάδας έργου
- 2022-2023 EMBO Workshop entitled “Systems biology: Linking chromatin and epigenetics to disease and development” ΠΚ: ΕΥ για το ΔΠΘ
- 2022-2023 Ανάδειξη οινικής ταυτότητας του νομού Δράμας μέσα από ολιστικό χαρακτηρισμό του φυσικού και μικροβιακού περιβάλλοντος-DRAMA TERROIR, Δράση «Ερευνώ-Δημιουργώ-Καινοτομώ ΕΣΠΑ, ΓΓΕΤ. ΕΥ για το ΔΠΘ: Καθηγήτρια Μαριρένα Γρηγορίου ΠΚ: Μέλος ομάδας έργου
- 2021 Διμερείς σχέσεις του Δημοκρίτειου Πανεπιστημίου της Θράκης με το Ερευνητικό Ινστιτούτο Matis στην Ισλανδία, ΥΠΕΝ ΕΥ για το ΔΠΘ: Καθηγητής Ραφαήλ Σανδαλτζόπουλος ΠΚ: Μέλος ομάδας έργου – Αναπληρωματικός ΕΥ
- 2021-2023 Μοριακή ταυτοποίηση και αξιοποίηση αυτόχθονων ποικιλιών λυκίσκου για την παραγωγή υψηλής ποιότητας ζύθων με ονομασία προέλευσης- ΠΑΖΛ (Παραγωγή Ανάλυση Ζύθων Λυκίσκου), Επιχειρησιακό Πρόγραμμα ΣΤΕΡΕΑ ΕΛΛΑΔΑ 2014 – 2020 ΓΓΕΤ. ΕΥ για το ΔΠΘ: Καθηγήτρια Μαριρένα Γρηγορίου ΠΚ: Μέλος ομάδας έργου – Αναπληρωματικός ΕΥ
- 2021-2023 AΓΡΟ4+ – Ολιστική προσέγγιση στη Γεωργία 4.0 για νέους αγρότες, Υποστήριξη της Περιφερειακής Αριστείας ΕΠΑΝΕΚ- ΓΓΕΤ. ΕΥ για το ΔΠΘ: Καθηγήτρια Μαριρένα Γρηγορίου ΠΚ: Μέλος ομάδας έργου
- 2021-2023 Εφαρμογές Μικροβιώματος σε συστήματα τροφίμων – Foodbiomes, Υποστήριξη της Περιφερειακής Αριστείας ΕΠΑΝΕΚ- ΓΓΕΤ ΕΥ για το ΔΠΘ: Καθηγητής Ιωάννης Κουρκουτάς ΠΚ: Μέλος ομάδας έργου
- 2021-2023 Αξιοποίηση του μικροβιακού terroir των αμπελώνων της εταιρείας Κτήμα Παυλίδη για την ανάδειξη των ιδιαίτερων ποιοτικών χαρακτηριστικών των τοπικών οίνων – PavlidisTerroir, Επιχειρησιακό Πρόγραμμα Ανατολικής Μακεδονίας & Θράκης 2014 – 2020 ΓΓΕΤ ΕΥ για το ΔΠΘ: Καθηγήτρια Μαριρένα Γρηγορίου ΠΚ: Μέλος ομάδας έργου
- Picco G, Cetin R, Bindels E, van Beek G, van IJcken WFJ, van den Hout M, Kolovos P, Mulugeta E, Huylebroeck D, Grosveld F. (2026). Functional analysis of two uncharacterized genes, C130074G19Rik and I830077J02Rik, during early hematopoietic development. J Cell Sci. Jan 15;139(2)
- Seufert I, Gerosa I, Varamogianni-Mamatsi V, Vladimirova A, Sen E, Mantz S, Rademacher A, Schumacher S, Liakopoulos P, Kolovos P, Anders S, Mallm JP, Papantonis A, Rippe K. (2026) Two distinct chromatin modules regulate proinflammatory gene expression. Nat Cell Biol. Jan;28(1):182-196
- Tsikitis M, Diokmetzidou A, Liakopoulos P, Karipidou M, Kokkinopoulos I, Vatsellas G, Kloukina I, Kolovos P, Capetanaki Y. (2025). Molecular insights into the role of desmin intermediate filament network in chromatin landscape, cardiomyocyte differentiation, and maturation. Cell Death Dis. Oct 16;16(1):723.
- Tokamani M, Liakopoulos P, Tegopoulos K, Zigkou AM, Triantaphyllidis G, Kamidis N, Grigoriou ME, Sandaltzopoulos R, Kolovos P. # (2025). Spatiotemporal Dynamics of Microbial and Fish Communities in the Thracian Sea Revealed by eDNA Metabarcoding. Microorganisms. Oct 15;13(10):2373.
- Papatheodorou I, Blažková G, Bosáková V, Tomášiková Z, Spearing E, Klieber R, Ostašov P, Štíchová J, Dvončová M, Mýtniková A, Emmer J, Bendíčková K, Tomáš T, Šrámek V, Kolovos P, Holubová M, Helán M, Vlková M, Frič J, Hortová-Kohoutková M. (2025). Redefining the role of IL-18 in post-surgical recovery and sepsis: a key mediator of inflammation resolution. J Transl Med. Jul 2;23(1):728.
- Bartusel M, Kim SX, Rehimi R, Darnell AM, Nikolić M, Heggemann J, Kolovos P, van Ijcken WFJ, Varineau J, Crispatzu G, Mangold E, Brugmann SA, Vander Heiden MG, Laugsch M, Ludwig KU, Rada-Iglesias A, Calo E. (2025). A non-syndromic orofacial cleft risk locus links tRNA splicing defects to neural crest cell pathologies. Am J Hum Genet. May 1;112(5):1097-1116.
- Tegopoulos, K., Polychronidou, S.V., Voumvouraki, A., Kolovos, P., Skavdis, G., Grigoriou, M.E. (2025). Precise Identification of Vitis vinifera L. Varieties Using Cost-Effective NGS-Based SNP Genotyping.Horticulturae 11(4), 375;
- Bosáková, V., Papatheodorou, I., Kafka, F., Tomášiková, Z., Kolovos, P., Hortová Kohoutková, M., & Frič, J. (2025). Serotonin attenuates tumor necrosis factor-induced intestinal inflammation by intercting with human mucosal tissue. Experimental & molecular medicine Feb;57(2):364-378
- Tasis, A., Papaioannou, N. E., Grigoriou, M., Paschalidis, N., Loukogiannaki, K., Filia, A,…, Liakopoulos, P., Liapis, K., Kolovos, P., Chavakis, T., Alissafi, T., Kotsianidis, I., Mitroulis, I. (2024). Single-cell analysis of bone marrow CD8+ T cells in Myeloid Neoplasms predicts response to treatment with Azacitidine. Cancer research communications, 4(12),
- Tegopoulos, K., Tsirka, T., Stekas, C., Gerasimidi, E., Skavdis, G., Kolovos, P.#, Grigoriou, M.E.#. (2024) Spatiotemporal Dynamics of Assyrtiko Grape Microbiota. Microorganisms, 12(3):577.
- Tsetsos, F., Topaloudi, A., Jain, P., Yang, Z., Yu, D., Kolovos, P., Tumer, Z., … Paschou, P. (2024). Genome-wide Association Study Points to Novel Locus for Gilles de la Tourette Syndrome. Biological psychiatry, 96(2), 114–124.
- Tegopoulos, K., Fountas, D.V., Andronidou, E-M., Bagos, P.G., Kolovos, P., Skavdis, G., Pergantas, P., Braliou, G.G., Papageorgiou, A.C., Grigoriou, M.E. (2023) Assessing Genetic Diversity and Population Differentiation in Wild Hop (Humulus lupulus) from the Region of Central Greece via SNP-NGS Genotyping. Diversity, 15(12):1171.
- Varsamis, G. D., Karafyllidis, I. G., Gilkes, K. M., Arranz, U., Martin-Cuevas, R., Calleja, G., Dimitrakis, P., Kolovos, P., Sandaltzopoulos, R., Jessen, H. C., & Wong, J. (2023). Quantum gate algorithm for reference-guided DNA sequence alignment. Computational biology and chemistry, 107, 107959.
- Varsamis, G. D., Karafyllidis, I. G., Gilkes, K. M., Arranz, U., Martin-Cuevas, R., Calleja, G., Wong, J., Jessen, H. C., Dimitrakis, P., Kolovos, P., & Sandaltzopoulos, R. (2023). Quantum algorithm for de novo DNA sequence assembly based on quantum walks on graphs. Bio Systems, 233, 105037.
- Mitropoulou, G., Prapa, I., Nikolaou, A., Tegopoulos, K., Tsirka, T., Chorianopoulos, N., Tassou, C., Kolovos, P., Grigoriou, M. E., & Kourkoutas, Y. (2022). Effect of Free or Immobilized Lactiplantibacillus plantarum T571 on Feta-Type Cheese Microbiome. Frontiers in bioscience (Elite edition), 14(4), 31.
- Foutadakis, S., Roupakia, E., Liakopoulos, P., Kolovos, P.#, & Kolettas, E#. (2022). An Expanded Interplay Network between NF-κB p65 (RelA) and E2F1 Transcription Factors: Roles in Physiology and Pathology. Cancers, 14(20), 5047.
- Kiousi, D. E., Efstathiou, C., Tegopoulos, K., Mantzourani, I., Alexopoulos, A., Plessas, S., Kolovos, P., Koffa, M., & Galanis, A. (2022). Genomic Insight Into Lacticaseibacillus paracasei SP5, Reveals Genes and Gene Clusters of Probiotic Interest and Biotechnological Potential. Frontiers in microbiology, 13, 922689.
- Schilders, K. A. A., Edel, G. G., Eenjes, E., Oresta, B., Birkhoff, J., Boerema-de Munck, A., Buscop-van Kempen, M., Liakopoulos, P., Kolovos, P., Demmers, J. A. A., Poot, R., Wijnen, R. M. H., Tibboel, D., & Rottier, R. J. (2022). Identification of SOX2 Interacting Proteins in the Developing Mouse Lung With Potential Implications for Congenital Diaphragmatic Hernia. Frontiers in pediatrics, 10, 881287.
- Tegopoulos, K., Stergiou, O. S., Kiousi, D. E., Tsifintaris, M., Koletsou, E., Papageorgiou, A. C., Argyri, A. A., Chorianopoulos, N., Galanis, A.#, & Kolovos, P.# (2021). Genomic and Phylogenetic Analysis of Lactiplantibacillus plantarum L125, and Evaluation of Its Anti-Proliferative and Cytotoxic Activity in Cancer Cells. Biomedicines, 9(11), 1718.
- Stergiou, O. S., Tegopoulos, K., Kiousi, D. E., Tsifintaris, M., Papageorgiou, A. C., Tassou, C. C., Chorianopoulos, N., Kolovos, P.#, & Galanis, A.# (2021). Whole-Genome Sequencing, Phylogenetic and Genomic Analysis of Lactiplantibacillus pentosus L33, a Potential Probiotic Strain Isolated From Fermented Sausages. Frontiers in microbiology, 12, 746659.
- Boltsis, I., Grosveld, F., Giraud, G.#, & Kolovos, P.# (2021). Chromatin Conformation in Development and Disease. Frontiers in cell and developmental biology, 9, 723859.
- Giraud, G.*, Kolovos, P.*, Boltsis, I., van Staalduinen, J., Guyot, B., Weiss-Gayet, M., IJcken, W. V., Morlé, F., & Grosveld, F. (2021). Interplay between FLI-1 and the LDB1 complex in murine erythroleukemia cells and during megakaryopoiesis. iScience, 24(3), 102210.
- Boltsis I, Nowosad K, Brouwer RWW, Tylzanowski P, van IWFJ, Huylebroeck D, Grosveld F, Kolovos P.(2021). Low Input Targeted Chromatin Capture (Low-T2C). Methods Mol Biol 2351: 165-179.
- Birkhoff, J. C., Brouwer, R. W. W., Kolovos, P., Korporaal, A. L., Bermejo-Santos, A., Boltsis, I., Nowosad, K., van den Hout, M. C. G. N., Grosveld, F. G., van IJcken, W. F. J., Huylebroeck, D., & Conidi, A. (2020). Targeted chromatin conformation analysis identifies novel distal neural enhancers of ZEB2 in pluripotent stem cell differentiation. Human molecular genetics, 29(15), 2535–2550.
- Kolovos, P.*, Nishimura, K.*, Sankar, A.*, Sidoli, S., Cloos, P. A., Helin, K., & Christensen, J. (2020). PR-DUB maintains the expression of critical genes through FOXK1/2- and ASXL1/2/3-dependent recruitment to chromatin and H2AK119ub1 deubiquitination. Genome research, 30(8), 1119–1130.
- Yu, X., Martella, A., Kolovos, P., Stevens, M., Stadhouders, R., Grosveld, F. G., & Andrieu-Soler, C. (2020). The dynamic emergence of GATA1 complexes identified in in vitro embryonic stem cell differentiation and in vivo mouse fetal liver. Haematologica, 105(7), 1802–1812.
- Laugsch, M., Bartusel, M., Rehimi, R., Alirzayeva, H., Karaolidou, A., Crispatzu, G., Zentis, P., Nikolic, M., Bleckwehl, T., Kolovos, P., van Ijcken, W. F. J., Šarić, T., Koehler, K., Frommolt, P., Lachlan, K., Baptista, J., & Rada-Iglesias, A. (2019). Modeling the Pathological Long-Range Regulatory Effects of Human Structural Variation with Patient-Specific hiPSCs. Cell stem cell, 24(5), 736–752.e12.
- Kolovos, P.#, Brouwer, R. W. W., Kockx, C. E. M., Lesnussa, M., Kepper, N., Zuin, J., Imam, A. M. A., van de Werken, H. J. G., Wendt, K. S., Knoch, T. A.#, van IJcken, W. F. J., & Grosveld, F.# (2018). Investigation of the spatial structure and interactions of the genome at sub-kilobase-pair resolution using T2C. Nature protocols, 13(3), 459–477.
- Zuin, J., Casa, V., Pozojevic, J., Kolovos, P., van den Hout, M. C. G. N., van Ijcken, W. F. J., Parenti, I., Braunholz, D., Baron, Y., Watrin, E., Kaiser, F. J., & Wendt, K. S. (2017). Regulation of the cohesin-loading factor NIPBL: Role of the lncRNA NIPBL-AS1 and identification of a distal enhancer element. PLoS genetics, 13(12), e1007137.
- Chondrou, V., Kolovos, P., Sgourou, A., Kourakli, A., Pavlidaki, A., Kastrinou, V., John, A., Symeonidis, A., Ali, B. R., Papachatzopoulou, A., Katsila, T., & Patrinos, G. P. (2017). Whole transcriptome analysis of human erythropoietic cells during ontogenesis suggests a role of VEGFA gene as modulator of fetal hemoglobin and pharmacogenomic biomarker of treatment response to hydroxyurea in β-type hemoglobinopathy patients. Human genomics, 11(1), 24.
- Cruz-Molina, S., Respuela, P., Tebartz, C., Kolovos, P., Nikolic, M., Fueyo, R., van Ijcken, W. F. J., Grosveld, F., Frommolt, P., Bazzi, H., & Rada-Iglesias, A. (2017). PRC2 Facilitates the Regulatory Topology Required for Poised Enhancer Function during Pluripotent Stem Cell Differentiation. Cell stem cell, 20(5), 689–705.e9.
- Knoch, T. A., Wachsmuth, M., Kepper, N., Lesnussa, M., Abuseiris, A., Ali Imam, A. M., Kolovos, P., Zuin, J., Kockx, C. E. M., Brouwer, R. W. W., van de Werken, H. J. G., van IJcken, W. F. J., Wendt, K. S., & Grosveld, F. G. (2016). The detailed 3D multi-loop aggregate/rosette chromatin architecture and functional dynamic organization of the human and mouse genomes. Epigenetics & chromatin, 9, 58.
- Brant, L., Georgomanolis, T., Nikolic, M., Brackley, C. A., Kolovos, P., van Ijcken, W., Grosveld, F. G., Marenduzzo, D., & Papantonis, A. (2016). Exploiting native forces to capture chromosome conformation in mammalian cell nuclei. Molecular systems biology, 12(12), 891.
- Kolovos, P.#, Georgomanolis, T., Koeferle, A., Larkin, J. D., Brant, L., Nikolicć, M., Gusmao, E. G., Zirkel, A., Knoch, T. A., van Ijcken, W. F., Cook, P. R., Costa, I. G., Grosveld, F. G., & Papantonis, A.#(2016). Binding of nuclear factor κB to noncanonical consensus sites reveals its multimodal role during the early inflammatory response. Genome research, 26(11), 1478–1489.
- Stadhouders, R., Cico, A., Stephen, T., Thongjuea, S., Kolovos, P., Baymaz, H. I., Yu, X., Demmers, J., Bezstarosti, K., Maas, A., Barroca, V., Kockx, C., Ozgur, Z., van Ijcken, W., Arcangeli, M. L., Andrieu-Soler, C., Lenhard, B., Grosveld, F., & Soler, E. (2015). Control of developmentally primed erythroid genes by combinatorial co-repressor actions. Nature communications, 6, 8893.
- Ferri, F., Parcelier, A., Petit, V., Gallouet, A. S., Lewandowski, D., Dalloz, M., van den Heuvel, A., Kolovos, P., Soler, E., Squadrito, M. L., De Palma, M., Davidson, I., Rousselet, G., & Romeo, P. H. (2015). TRIM33 switches off Ifnb1 gene transcription during the late phase of macrophage activation. Nature communications, 6, 8900.
- Caputo, L., Witzel, H. R., Kolovos, P., Cheedipudi, S., Looso, M., Mylona, A., van IJcken, W. F., Laugwitz, K. L., Evans, S. M., Braun, T., Soler, E., Grosveld, F., & Dobreva, G. (2015). The Isl1/Ldb1 Complex Orchestrates Genome-wide Chromatin Organization to Instruct Differentiation of Multipotent Cardiac Progenitors. Cell stem cell, 17(3), 287–299.
- Tresini, M., Warmerdam, D. O., Kolovos, P., Snijder, L., Vrouwe, M. G., Demmers, J. A., van IJcken, W. F., Grosveld, F. G., Medema, R. H., Hoeijmakers, J. H., Mullenders, L. H., Vermeulen, W., & Marteijn, J. A. (2015). The core spliceosome as target and effector of non-canonical ATM signalling. Nature, 523(7558), 53–58.
- Diermeier, S.*, Kolovos, P.*, Heizinger, L., Schwartz, U., Georgomanolis, T., Zirkel, A., Wedemann, G., Grosveld, F., Knoch, T. A., Merkl, R., Cook, P. R., Längst, G., & Papantonis, A. (2014). TNFα signalling primes chromatin for NF-κB binding and induces rapid and widespread nucleosome repositioning. Genome biology, 15(12), 536.
- Kolovos, P., van de Werken, H. J., Kepper, N., Zuin, J., Brouwer, R. W., Kockx, C. E., Wendt, K. S., van IJcken, W. F., Grosveld, F., & Knoch, T. A. (2014). Targeted Chromatin Capture (T2C): a novel high resolution high throughput method to detect genomic interactions and regulatory elements. Epigenetics & chromatin, 7, 10.
- Stadhouders, R., de Bruijn, M. J., Rother, M. B., Yuvaraj, S., Ribeiro de Almeida, C., Kolovos, P., Van Zelm, M. C., van Ijcken, W., Grosveld, F., Soler, E., & Hendriks, R. W. (2014). Pre-B cell receptor signaling induces immunoglobulin κ locus accessibility by functional redistribution of enhancer-mediated chromatin interactions. PLoS biology, 12(2), e1001791.
- Zuin, J., Dixon, J. R., van der Reijden, M. I., Ye, Z., Kolovos, P., Brouwer, R. W., van de Corput, M. P., van de Werken, H. J., Knoch, T. A., van IJcken, W. F., Grosveld, F. G., Ren, B., & Wendt, K. S. (2014). Cohesin and CTCF differentially affect chromatin architecture and gene expression in human cells. Proceedings of the National Academy of Sciences of the United States of America, 111(3), 996–1001.
- Stadhouders, R.*, Kolovos, P.*, Brouwer, R.*, Zuin, J., van den Heuvel, A., Kockx, C., Palstra, R. J., Wendt, K. S., Grosveld, F., van Ijcken, W., & Soler, E. (2013). Multiplexed chromosome conformation capture sequencing for rapid genome-scale high-resolution detection of long-range chromatin interactions. Nature protocols, 8(3), 509–524.
- Stadhouders, R., van den Heuvel, A., Kolovos, P., Jorna, R., Leslie, K., Grosveld, F., & Soler, E. (2012). Transcription regulation by distal enhancers: who’s in the loop?. Transcription, 3(4), 181–186.
- van den Driesche, S., Kolovos, P., Platts, S., Drake, A. J., & Sharpe, R. M. (2012). Inter-relationship between testicular dysgenesis and Leydig cell function in the masculinization programming window in the rat. PloS one, 7(1), e30111.
- Kolovos, P., Knoch, T. A., Grosveld, F. G., Cook, P. R., & Papantonis, A. (2012). Enhancers and silencers: an integrated and simple model for their function. Epigenetics & chromatin, 5(1), 1.
| Ονοματεπώνυμο | Τίτλος | Επιβλέποντας | Έτος | Κατάσταση |
|---|---|---|---|---|
| Κωνσταντίνος Τεγόπουλος | Γονιδιωματική και μεταγονιδιωματική ανάλυση ειδών οικονομικής σημασίας στην αγροβιολογία | Μαριρένα Γρηγορίου - Πέτρος Κολοβός | 2025 | Ολοκληρωμένη |
| Ονοματεπώνυμο | Ιδιότητα |
|---|---|
| Παναγιώτης Λιακόπουλος | Υποψήφιος Διδάκτωρ |
| Αλεξάνδρα Γέρου | Υποψήφια Διδάκτωρ |
| Κάτια Κουφονικόλα | Υποψήφια Διδάκτωρ |
| Κωνσταντίνα Καραμητσου | Μεταπτυχιακή Φοιτήτρια |
| Νίκος Γιαννακοπουλος | Μεταπτυχιακός Φοιτητής |
| Ιωάννης Νασόπουλος | Μεταπτυχιακός Φοιτητής |
| Τρύφων Δημητρίου | Προπτυχιακός Φοιτητής |
| Ευθυμία-Δαναη Τζάνα | Προπτυχιακή Φοιτήτρια |
| Παναγιώτης Χριστοδουλόπουλος | Προπτυχιακός Φοιτητής |
| Ονοματεπώνυμο | Ιδιότητα |
|---|---|
| Κωνσταντίνος Τεγόπουλος | Διδάκτωρ |
| Χρήστος Κύργιος | Μεταπτυχιακός Φοιτητής |
| Δημήτρης Κοσπανός | Μεταπτυχιακός Φοιτητής |
| Μαρία Ανδρεάδου | Μεταπτυχιακή Φοιτήτρια |
| Πελαγία Χόνδρου | Μεταπτυχιακή Φοιτήτρια |
| Ευθυμία Βασιλίνα Κατσίκα | Μεταπτυχιακή Φοιτήτρια |
| Παρασκευή Κουτρα | Μεταπτυχιακή Φοιτήτρια |
| Νικόλαος Λότσιος | Μεταπτυχιακός Φοιτητής |
| Ιωάννα Παπαθεοδώρου | Μεταπτυχιακή Φοιτήτρια |
| Σταύρος Βιρβίλης | Μεταπτυχιακός Φοιτητής |
| Μαριάννα Γρινιεζάκη | Μεταπτυχιακή Φοιτήτρια |
| Ελίζα Κοτρίδου | Μεταπτυχιακή Φοιτήτρια |
| Σουζάνα Λογοθέτη | Μεταπτυχιακή Φοιτήτρια |
| Μαρία Γαιτανίδου | Μεταπτυχιακή Φοιτήτρια |
| Αθανασία Γκίκα | Μεταπτυχιακή Φοιτήτρια |
| Μαρία Μελισσουργού | Μεταπτυχιακή Φοιτήτρια |
| Αναστασία Μπούτσικα | Μεταπτυχιακή Φοιτήτρια |
| Ραφαέλα Μυλωνά | Μεταπτυχιακή Φοιτήτρια |
| Αικατερίνη Σκέυα | Μεταπτυχιακή Φοιτήτρια |
| Οδυσσέας Σωτήριος Στεργίου | Προπτυχιακός Φοιτητής |
| Ελισάβετ Καπετάνου | Προπτυχιακή Φοιτήτρια |
| Αγγελική Πανέτσου | Προπτυχιακή Φοιτήτρια |
| Σπυριδούλα Σαγροπούλου | Προπτυχιακή Φοιτήτρια |
| Μαρκέλα Ηλιδάκη | Προπτυχιακή Φοιτήτρια |
| Ελένη Μπάλλα | Προπτυχιακή Φοιτήτρια |
| Χρίστος Κιτσόπουλος | Προπτυχιακός Φοιτητής |
| Παύλος Τσιάρτας | Προπτυχιακός Φοιτητής |
| Κισάρα Γκιολένα | Προπτυχιακή Φοιτήτρια |
| Μιμτσουδης Σπυρίδων | Προπτυχιακός Φοιτητής |
| Ζαμπουρίδου Κωνσταντίνα | Προπτυχιακή Φοιτήτρια |
Πληροφορίες
Κολοβός Πέτρος, Αναπληρωτής Καθηγητής
Τμήμα Μοριακής Βιολογίας & Γενετικής, Δημοκρίτειο Πανεπιστήμιο Θράκης, Δραγάνα, Αλεξανδρούπολη